Was sind DNA-Mismatch-Reparatur (MMR) und Mikrosatelliteninstabilität (MSI)?
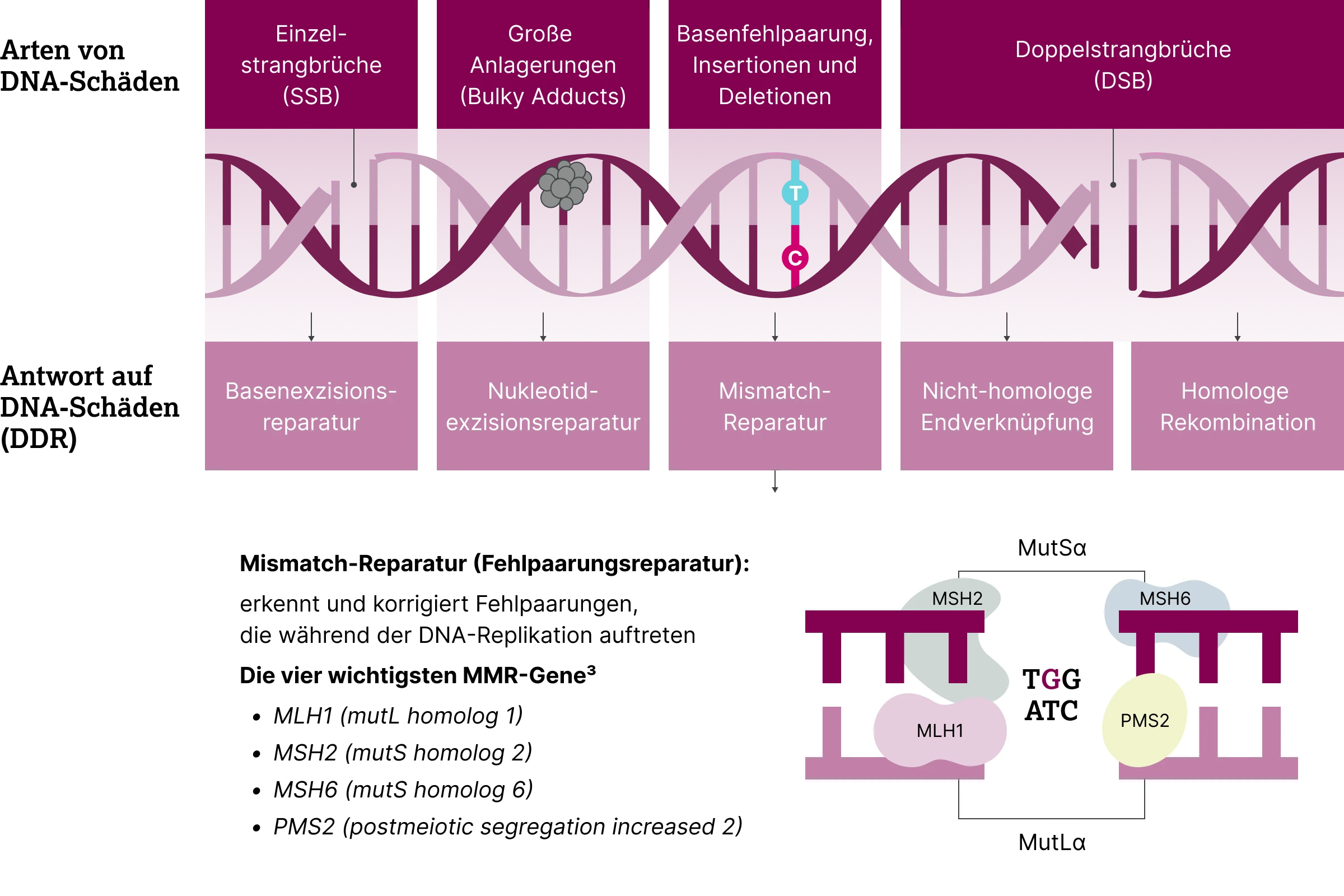
Die DNA-Mismatch-Reparatur (MMR) ist ein essenzieller zellulärer Mechanismus zur Korrektur von Basenfehlpaarungen, Insertionen oder Deletionen, die während der DNA-Replikation entstehen.1,2
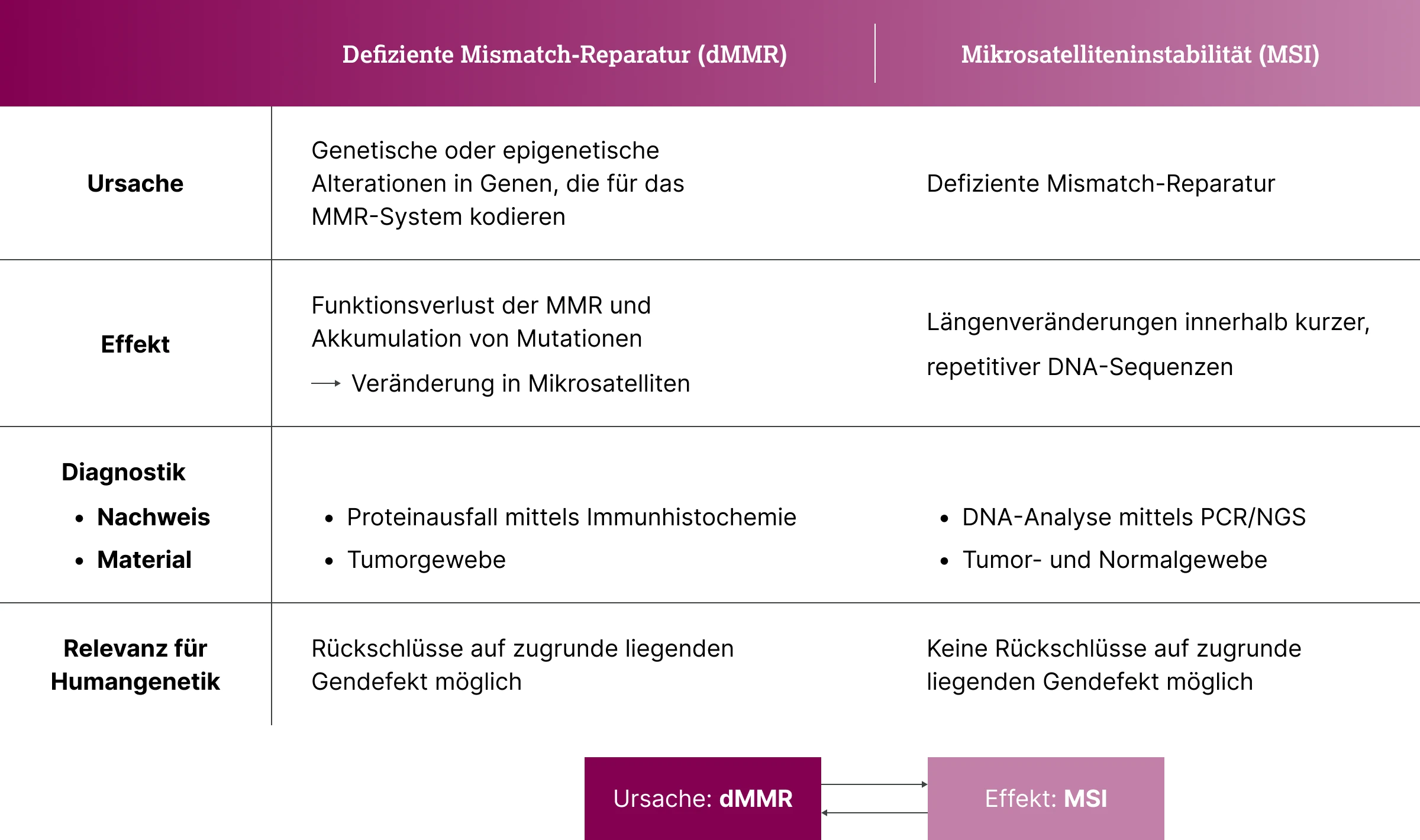
Eine intakte DNA-Reparatur wird als profiziente Mismatch-Reparatur (pMMR) bezeichnet, während eine fehlerhafte Reparatur als defiziente Mismatch-Reparatur (dMMR) klassifiziert wird. Eine dMMR entsteht durch genetische oder epigenetische Veränderungen in Genen, die für zentrale MMR-Proteine codieren.3
Die gestörte Reparaturfunktion führt zu einer erhöhten Mutationsrate und ist mit bestimmten Krebserkrankungen wie dem Lynch-Syndrom sowie verschiedenen soliden Tumoren assoziiert.4,5 Eine häufige Folge der dMMR ist die Mikrosatelliteninstabilität (MSI). Dabei handelt es sich um Längenveränderungen kurzer, repetitiver DNA-Sequenzen (1–6 Basenpaare), die infolge unzureichender Korrektur von Replikationsfehlern entstehen.3 Auch MSI wird mit einem erhöhten Tumorrisiko in Verbindung gebracht.5
Obwohl dMMR und MSI eng miteinander korrelieren und eine hohe diagnostische Konkordanz aufweisen,6 stellen sie unterschiedliche molekulare Phänomene dar und sind als eigenständige Biomarker zu bewerten.
DNA-Mismatch-Reparatur (MMR)
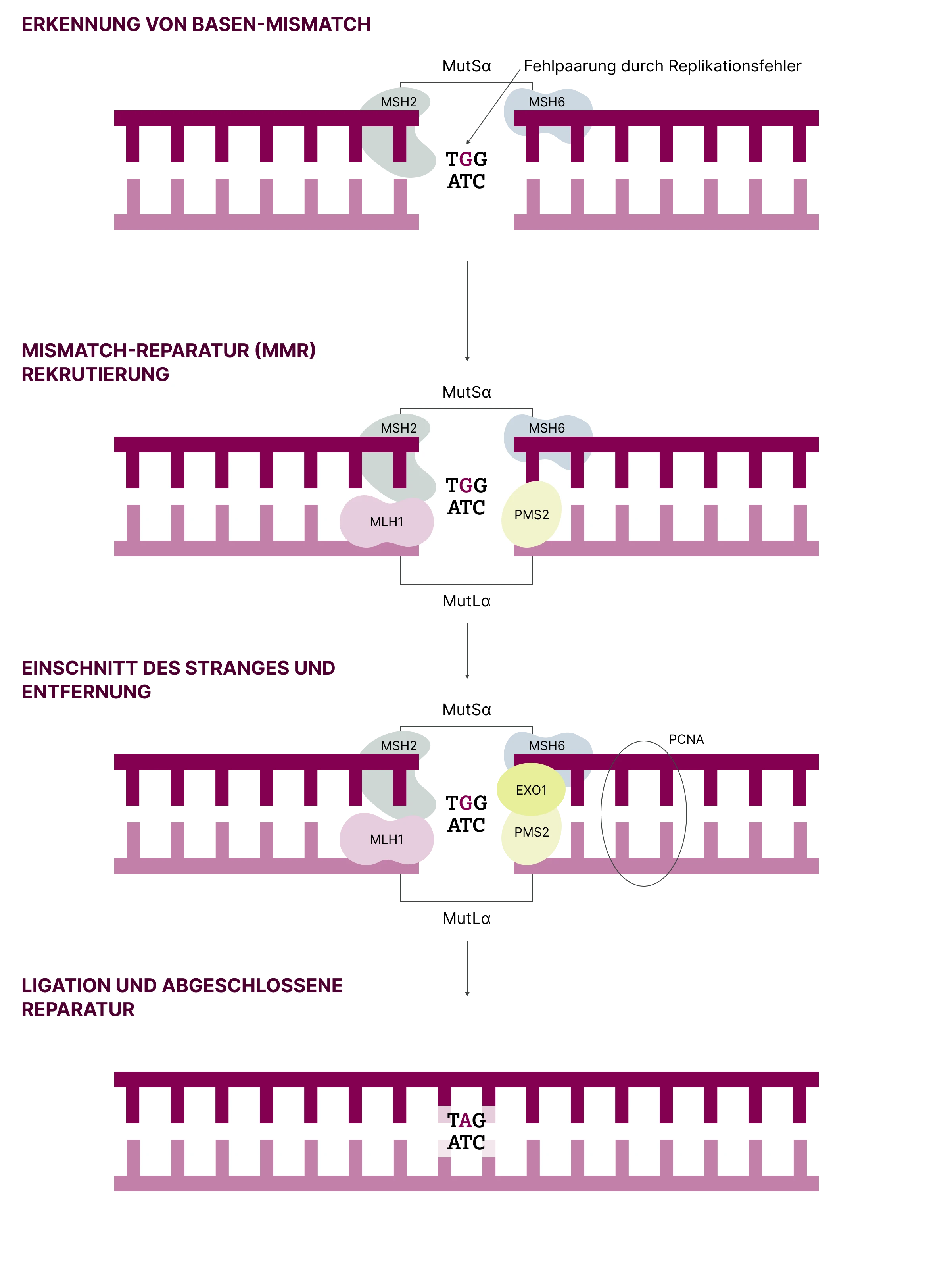
Die vier zentralen MMR-Gene – MLH1, MSH2, MSH6 und PMS2 – codieren für funktionelle Heterodimere: MutLα (MLH1–PMS2) und MutSα (MSH2–MSH6). Diese Proteinkomplexe sind essenziell für die Erkennung und Reparatur von Replikationsfehlern.3
Der Reparaturprozess verläuft in mehreren Schritten:
1. Erkennung:
Das MutSα-Heterodimer erkennt und bindet die Basenfehlpaarung.
2. Rekrutierung:
Das Proliferating-Cell Nuclear Antigen (PCNA) rekrutiert MutLα und positioniert es am beschädigten DNA-Strang.
3. Schnitt:
MutLα entfaltet Endonuklease-Aktivität und entfernt den fehlerhaften DNA-Abschnitt.
4. Austausch und Ligation:
Die Exonuklease EXO1 degradiert den beschädigten Strangabschnitt. Anschließend ergänzt die DNA-Polymerase δ die korrekten Nukleotide, und DNA-Ligase I schließt die verbleibende Lücke.
Bereits der Verlust eines der vier MMR-Gene führt zum Expressionsverlust des zugehörigen Proteins und resultiert in einer dMMR mit konsekutiver Beeinträchtigung der genomischen Integrität.3
Mikrosatelliteninstabilität (MSI)
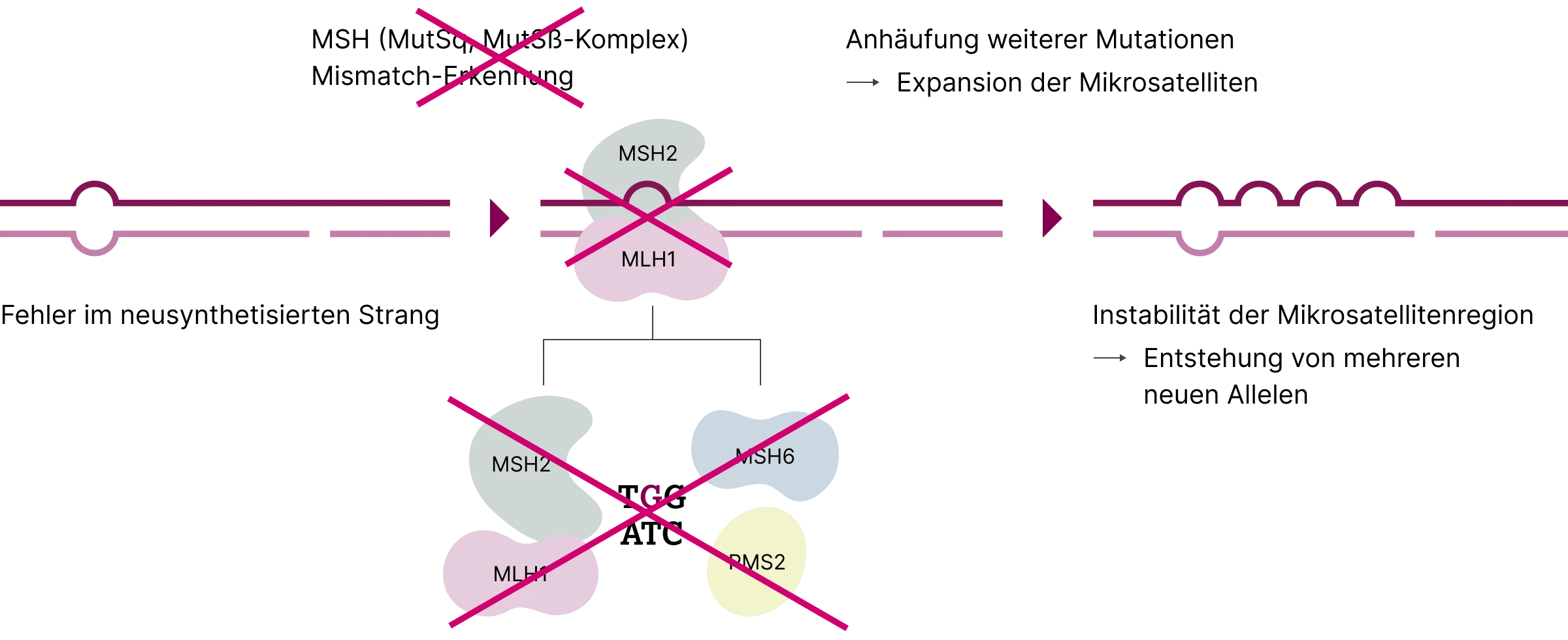
Fehlpaarungen, die z. B. bei der Zellteilung oder durch iatrogene Einflüsse entstehen, können bei Vorliegen einer dMMR nicht adäquat korrigiert werden.3 Besonders anfällig für solche Fehler sind Mikrosatelliten – kurze, repetitive DNA-Sequenzen –, deren Instabilität als MSI bezeichnet wird. MSI stellt einen phänotypischen Marker für eine dMMR dar.3 MSI ist von diagnostischer, prognostischer und prädiktiver Relevanz. Letztere betrifft insbesondere das Ansprechen auf Immuncheckpoint-Inhibitoren bei bestimmten Tumorentitäten.7
Der Nachweis von MSI erfolgt in der Regel durch Polymerase-Kettenreaktion (PCR)-basierte Verfahren oder mittels Next-Generation-Sequencing (NGS). Dabei werden Mikrosatellitenregionen im Tumorgewebe mit denen im korrespondierenden Normalgewebe verglichen. Längenveränderungen der amplifizierten Fragmente im Tumor im Vergleich zur Normalprobe weisen auf MSI hin. Dieses Verfahren erlaubt jedoch keine direkte Aussage über zugrunde liegende genetische Mutationen.9
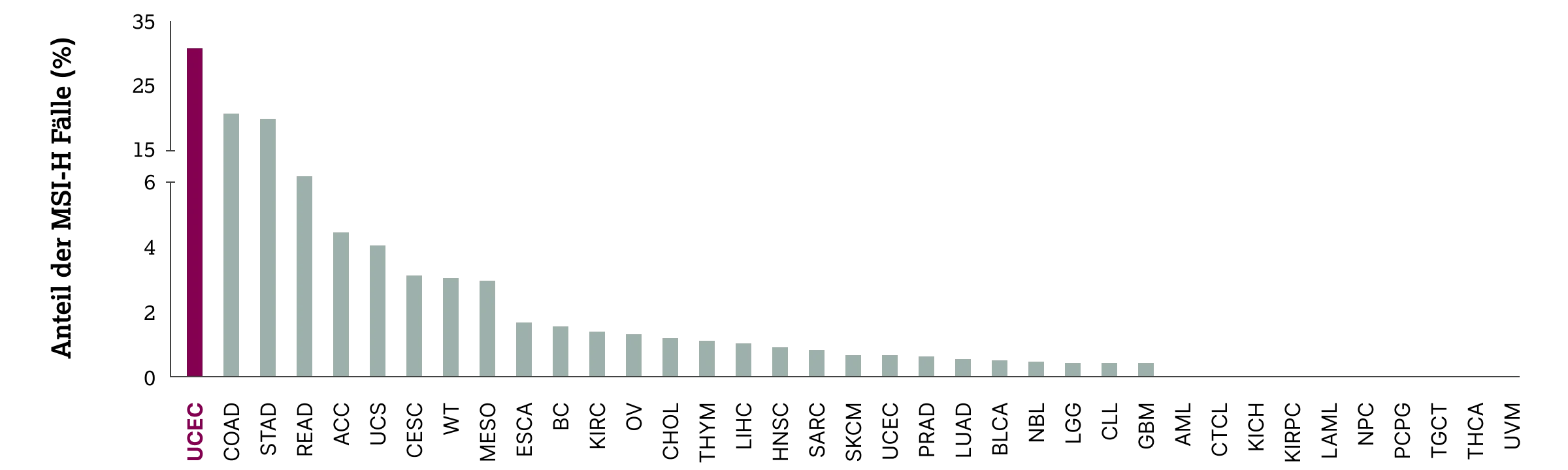
Beim Endometriumkarzinom wird in der aktuellen S3-Leitlinie empfohlen, eine MSI-Analyse nur bei unklaren Befunden der immunhistochemischen dMMR/pMMR-Diagnostik durchzuführen.10 Auch bei anderen Tumorentitäten ist MSI von diagnostischer und prognostischer Relevanz – insbesondere beim kolorektalen und beim Magen-Adenokarzinom.5
Abkürzungen
ACC: Nebennierenrindenkarzinom; AML: akute myeloische Leukämie bei Kindern (TARGET); BC: Mammakarzinom; BLCA: Harnblasenkarzinom; CESC: Zervikales Plattenepithel- und endozervikales Adenokarzinom; CHOL: Cholangiokarzinom; COAD: Kolon-Adenokarzinom; CTCL: Kutanes T-Zell-Lymphom; DDR: DNA-Damage-Response; DLBC: Diffus großzelliges B-Zell-Lymphom; dMMR: defiziente Mismatch-Reparatur; DNA: Desoxyribonukleinsäure; DSB: Doppelstrangbruch; ESCA: Ösophaguskarzinom; EXO1: Exonuklease; GBM: Glioblastoma multiforme; HNSC: Plattenepithelkarzinom des Kopf-Hals-Bereichs; KICH: chromophobes Nierenzellkarzinom; KIRC: klarzelliges Nierenzellkarzinom; KIRP: papilläres Nierenzellkarzinom; LAML: akute myeloische Leukämie (TCGA); LGG: low-grade Gliom; LIHC: hepatozelluläres Karzinom; MESO: Mesotheliom; MLH1: MutL Homolog 1; MMR: DNA-Mismatch-Reparatur; MSH2: Mutator S Homolog 2; MSH6: Mutator S Homolog 6; MSI: Mikrosatelliteninstabilität; MSI-H: hohe Mikrosatellitenstabilität; MutLα: Mutator L alpha; MutS: Mutator S; MutSα: Mutator S alpha; NBL: pädiatrisches Neuroblastom; NGS: Next-Generation-Sequencing; NPC: Nasopharynxkarzinom; OV: seröses Ovarialkarzinom; PAAD: Pankreas-Adenokarzinom; PCNA: Proliferating-Cell Nuclear Antigen; PCPG: Phäochromozytom und Paragangliom; PCR: Polymerase-Kettenreaktion; pMMR: profiziente Mismatch-Reparatur; PMS2: Postmeiotic Segregation Increased 2; PRAD: Prostata-Adenokarzinom; READ: Rektales Adenokarzinom; SARC: Sarkom; SKCM: kutanes malignes Melanom; SSB: Einzelstrangbruch; STAD: Magen-Adenokarzinom; TCGT: testikulärer Keimzelltumor; THCA: Schilddrüsenkarzinom; THYM: Thymom; UCEC: Endometriumkarzinom; UCS: Uteruskarzinosarkom; UVM: Uveales Melanom; WT: Wilms-Tumor
- Lord CJ, et al. Nature 2012;481(7381):287–94.
- Nickoloff JA. DNA Repair Dysregulation in Cancer. In: Wonk GT (Hrsg.) Stress response pathways in cancer. Dordrecht: Springer; 2014, p. 7–28.
- Luchini C, et al. Ann Oncol 2019;30(8):1232–43.
- Makker V, et al. Nat Rev Dis Primers 2021;7(1):88.
- Bonneville R, et al. JCO Precis Oncol 2017;1:PO.17.00073.
- Stelloo E, et al. Ann Oncol 2017;28(1):96–102.
- Curtius K, et al. Aliment Pharmacol Ther 2022;55(8):960–77.
- Alberts B, et al. Essential cell biology. Aufl. New York (USA): Norton & Company; 2023.
- Engel C, et al. Int J Cancer 2006;118(1):115–22.
- S3-Leitlinie Endometriumkarzinom. Version 3.0, Juni 2024. Verfügbar unter register.awmf.org/de/leitlinien/detail/032-034OL. Letzter Zugriff: Februar 2026.